简介
在 Stereo-seq 数据分析中,图像处理是生成准确 CellBin 的关键步骤。图像的质量、配准效果以及细胞分割的精度,都会直接影响到最终 CellBin 的准确性与下游分析结果。
在 SAW 流程中,自动分割算法通常可以识别大部分细胞的核边界,但在面对染色质量欠佳的图像时,分割效果可能会受到影响。即便进行了分割,结果往往不尽如人意,可能出现过分割、欠分割等问题。此外,针对一些特定场景,如图像 QC 失败无法自动配准,或FFPE 样本的 H&E 染色,SAW 流程目前默认不会进行自动细胞分割。这种情况下,如果需要获得 CellBin 矩阵,用户需要借助其他手段来补充分割步骤。
在分割效果不理想或缺失的情况下,为了获得更加精确、适合后续分析的细胞边界,StereoMap 提供了手动分割工具,用于修正局部区域的错误。然而,当需要处理大量样本时,手动修正变得低效且不现实。此时,结合第三方细胞分割算法(如 Cellpose、StarDist 或 DeepCell)生成自定义的分割 mask,并替换 SAW 的默认分割结果,是提高分割精度的有效途径。如此一来,能够重新计算优化后的 CellBin 矩阵,提升细胞边界的准确性,进而改善下游空间基因表达分析的可靠性。
此外,不同细胞分割算法在面对不同组织类型、染色方式或图像质量时可能呈现出差异化表现。实际应用中,可根据数据特征进行多种算法的尝试与比较,以获得更可靠的分割结果。接下来,我们将介绍如何将第三方分割结果整合进 StereoMap 与 SAW 工作流程中,从而重新生成优化后的 CellBin 矩阵。
前置准备
在开始操作之前,请确保您已经准备好以下内容:
SAW 分析结果 (
visualization.tar.gz)在 SAW 流程完成后,会在
/outs/目录下生成visualization.tar.gz文件,其中包含空间基因表达矩阵及相关可视化结果。将该文件下载并在本地解压后,可以看到
.gef矩阵、.stereo可视化文件等。如果在 SAW 流程中启用了自动图像分析,目录中还会包含.tar.gz图像文件。“配准后” 的TIFF 图像(
*_regist.tif)若由 SAW 流程进行了图像分析,会在
/outs/image找到配准后的 TIFF 图。若在 StereoMap Image Processing 中完成手动配准,您可以在您指定的输出目录中找到图像
.tar.gz和这张配准后的 TIFF 图。(请参考StereoMap手册 > 图像处理指南 > 核染色图像 (根据实际染色选择) > # 第二步:图像配准,完成手动图像-矩阵对齐)第三方分割必须基于此图(不可使用原始图),其尺寸和方向与空间矩阵一致。
第三方算法分割生成的二值化 TIFF mask
TIFF ,单通道灰度
uint8 类型二值图(1 = 细胞区域,0 = 背景)
尺寸、分辨率与
*_regist.tif完全一致基于
*_regist.tif生成分割 mask。请确保此 mask 满足以下要求:
StereoMap 桌面端软件 (版本 ≥ 4.0.0)
用于导入第三方分割生成的二值化 TIFF mask,在 Cell Segmentation 步骤中替换自动分割 mask,然后导出更新结果。
SAW 分析流程软件 (版本 ≥ 8.0.0)
在替换 mask 后,通过
SAW realign命令重新计算 CellBin 矩阵。
示例数据下载
您可以从我们的公开数据集中下载本文使用的示例数据。本示例为一份小鼠脑组织数据,可以从这里获取。相关信息如下:
芯片号:C04496D6
产品方案:时空转录组FFPE V1.0
染色方案:H&E染色
说明:由于默认自动图像处理不包含细胞分割,因此本案例需要借助第三方算法补充分割结果。本文中使用的 Cellpose-SAM 算法分割结果可以从 这里 获取。
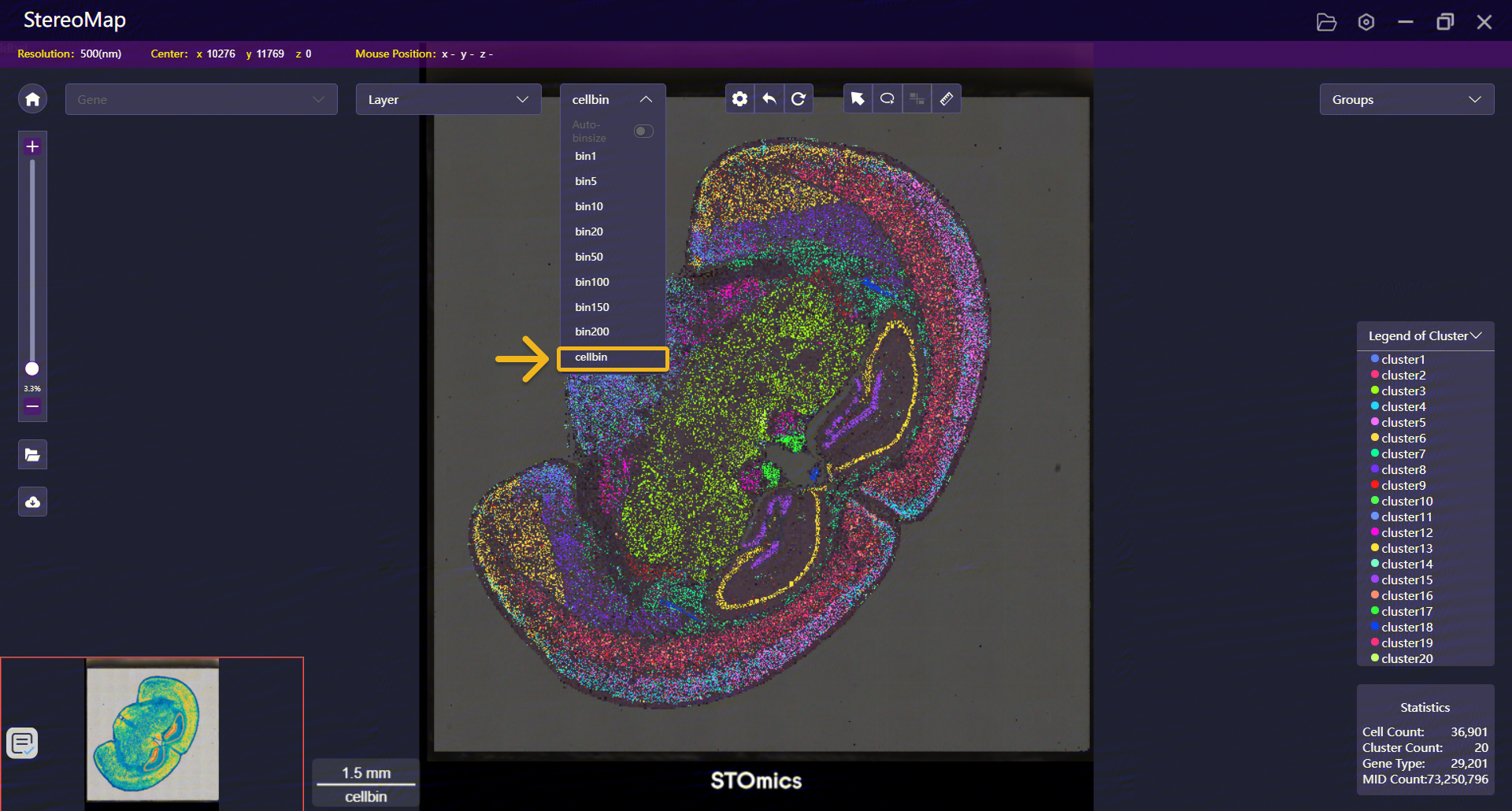
在StereoMap中导入图像
启动 StereoMap,打开 Image Processing 模块,选择染色类型并上传图像。
如果在 SAW 流程中已启用自动图像分析,推荐直接上传
.stereo文件,因为其包含配准信息。如果图像在 QC 阶段失败,或 SAW 分析时未使用图像,请上传
.tar.gz图像包。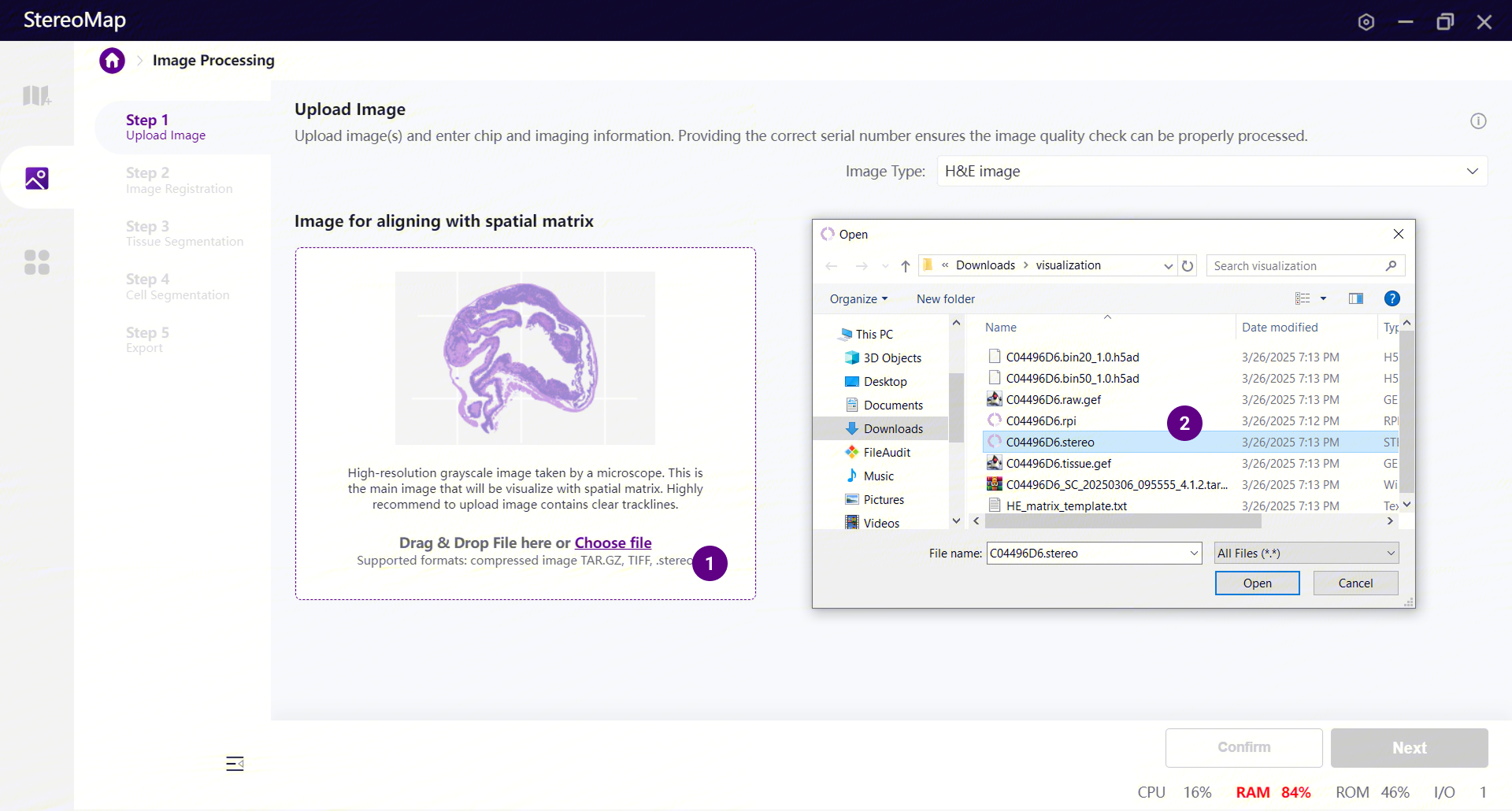
当上传的是
.stereo文件且配准无需调整时,可在 Step 2:Image Registration 中直接点击 Next,进入后续步骤。若自动配准存在偏差,或上传的是
.tar.gz文件,则需:在 Step 2 手动导入矩阵并进行配准(Morphology 或 Feature Point);
完成后,连续点击 Step 3 和 Step 4 的 Next,进入 Step 5:Export;
导出后将在目标目录生成
*_regist.tif文件。*_regist.tif图像与空间矩阵在尺寸与方向上完全一致。在后续的 CellBin 矩阵生成过程中,会基于像素坐标进行一对一映射。因此,在使用第三方工具进行细胞分割时,务必基于导出的*_regist.tif进行分割,并确保输出的二值化 mask 在尺寸、分辨率和方向与其完全一致。否则,在realign过程中可能出现细胞标注错位、区域偏移或 CellBin 计算异常等问题。
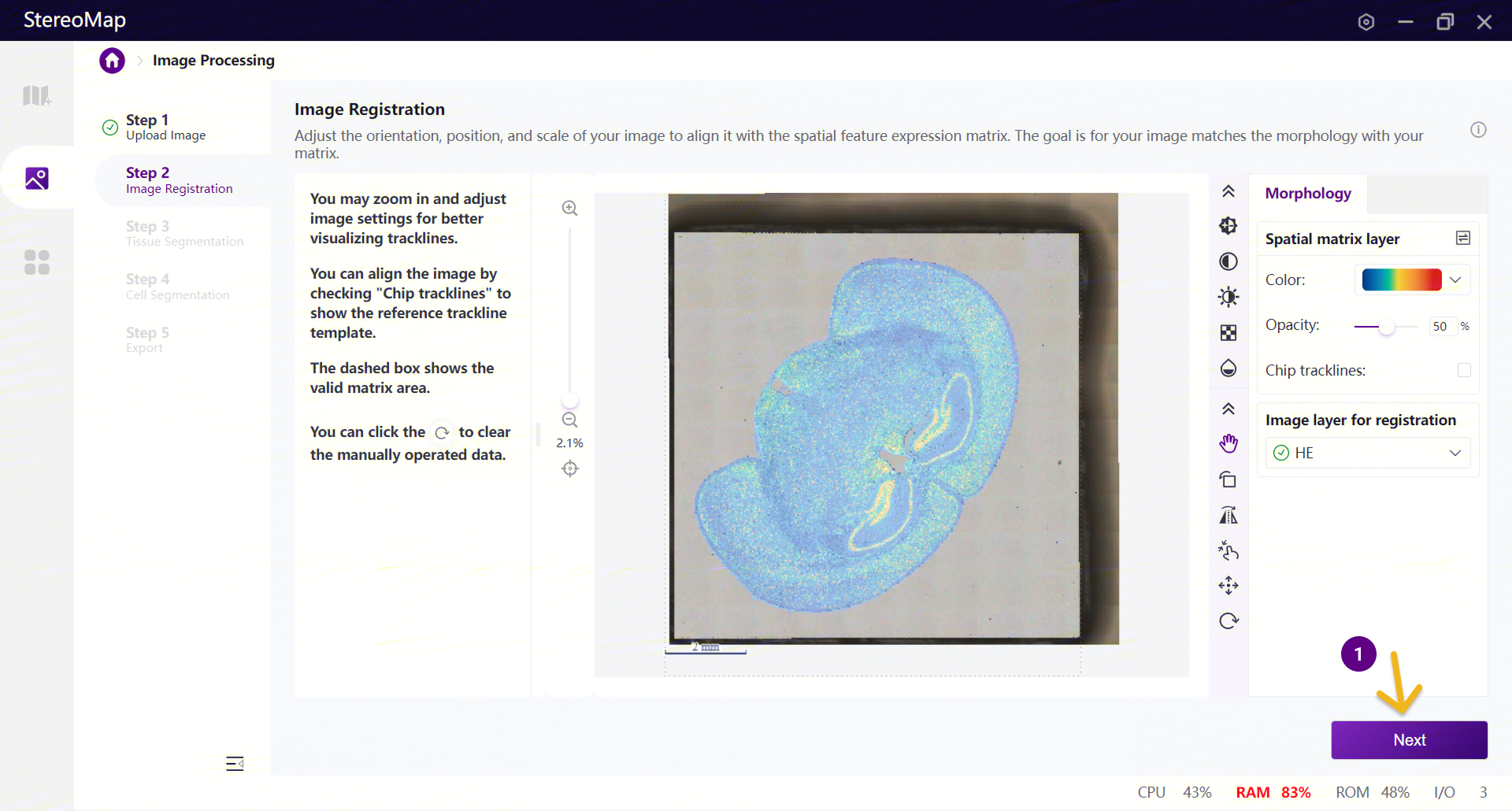
替换细胞分割 Mask
进入 Step 4:Cell Segmentation 模块。
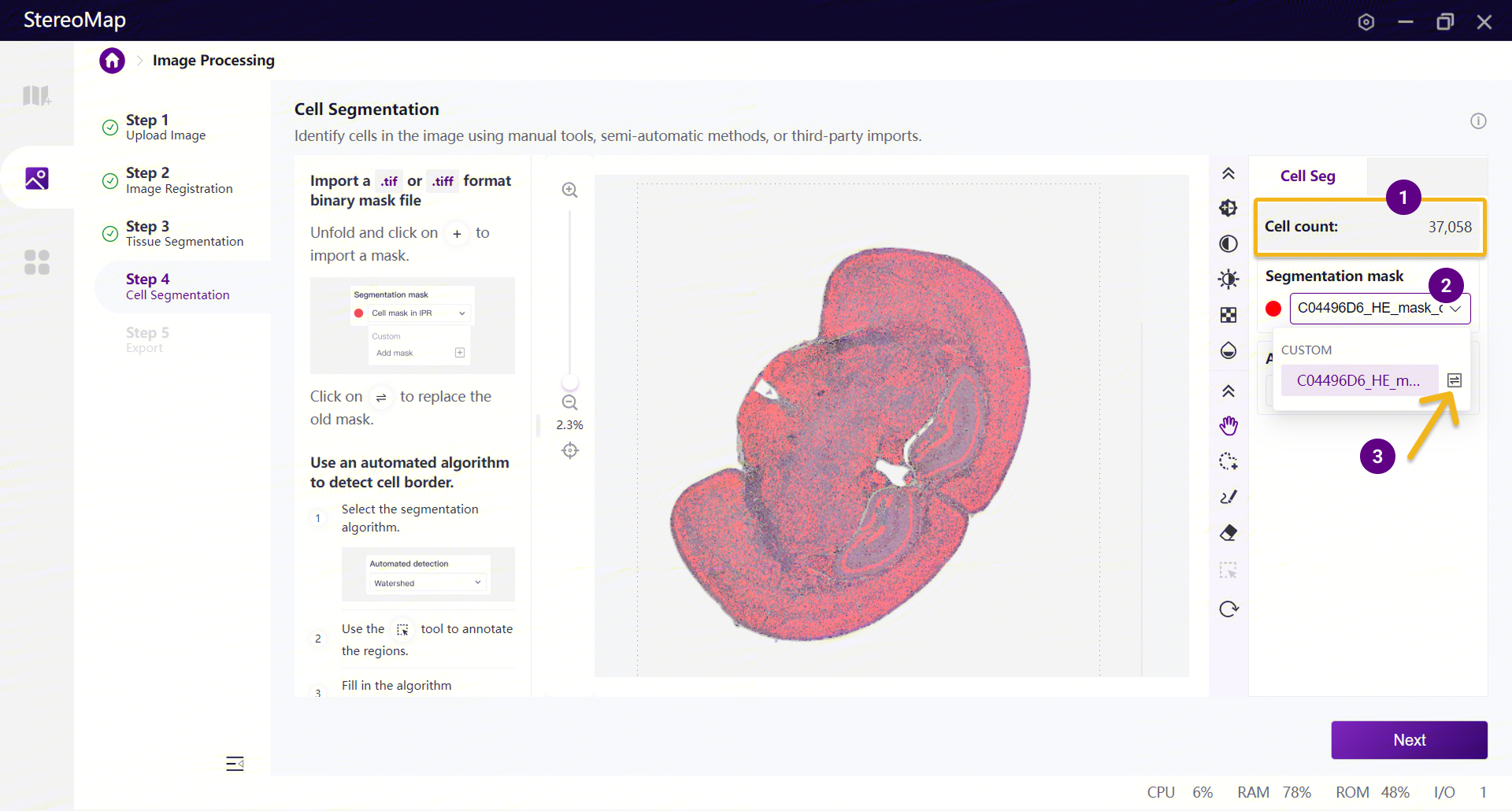
在 Segmentation mask 下拉框中,点击 Custom 下 Add mask 选项右侧的“+”添加 mask。在弹出的文件选择窗口中,选择由第三方工具生成的 TIFF mask。
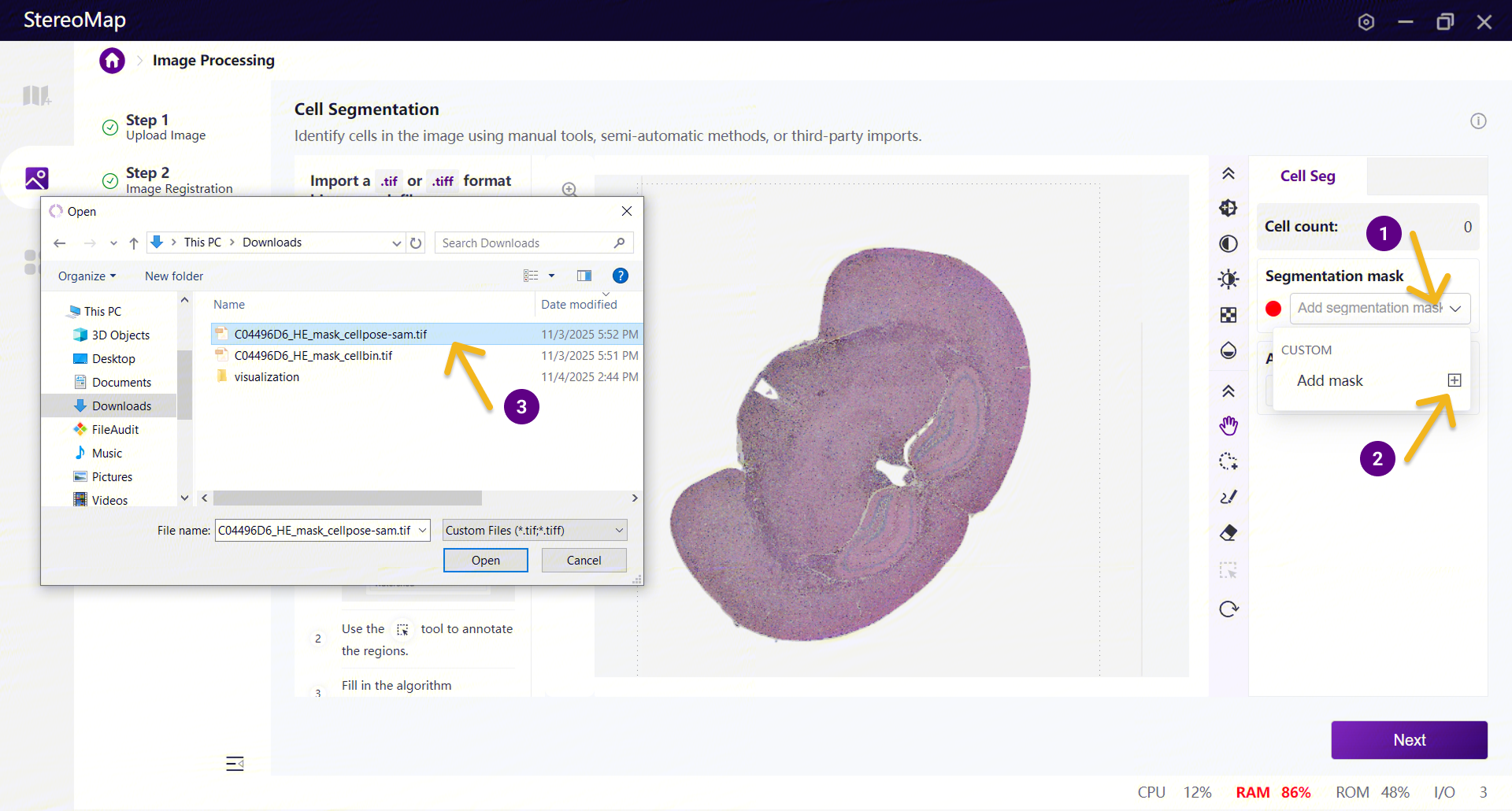
上传后,mask 会以细胞轮廓的形式显示在画布上,下方图层展示配准后的显微镜图像。用户可以放大画布仔细检查分割效果,也可使用手动编辑工具调整局部分割。上传新的 mask 后,软件会自动重新计算细胞数量。
如果已经上传了一个 mask,但检查后效果不理想,可再次打开 Segmentation mask 下拉框,点击 Custom下对应上次上传 mask 文件名右侧的 “←→” 图标,选择新的 TIFF mask 进行替换。
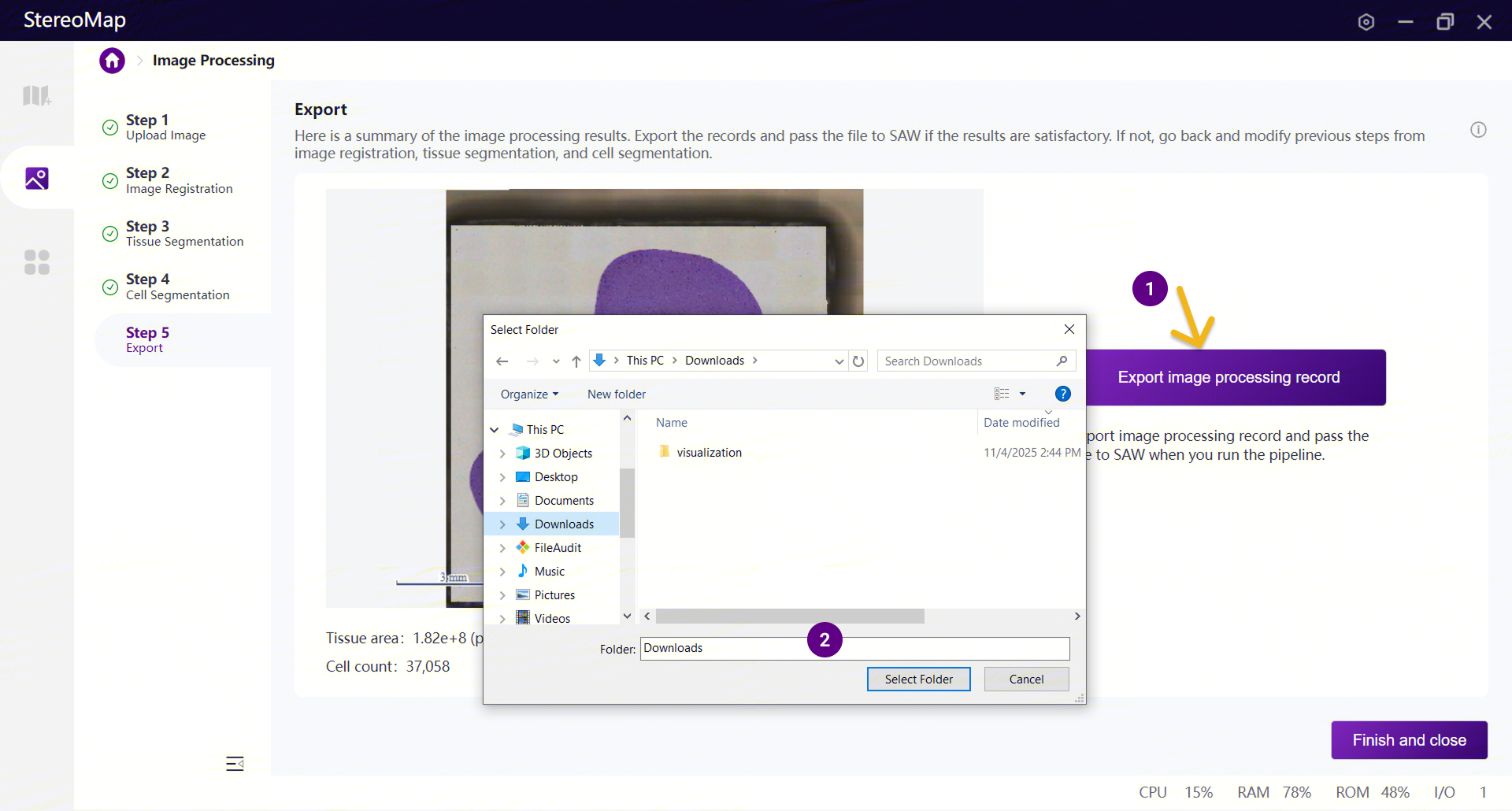
mask 替换完成后,进入Step 5。选择目标路径导出更新结果。
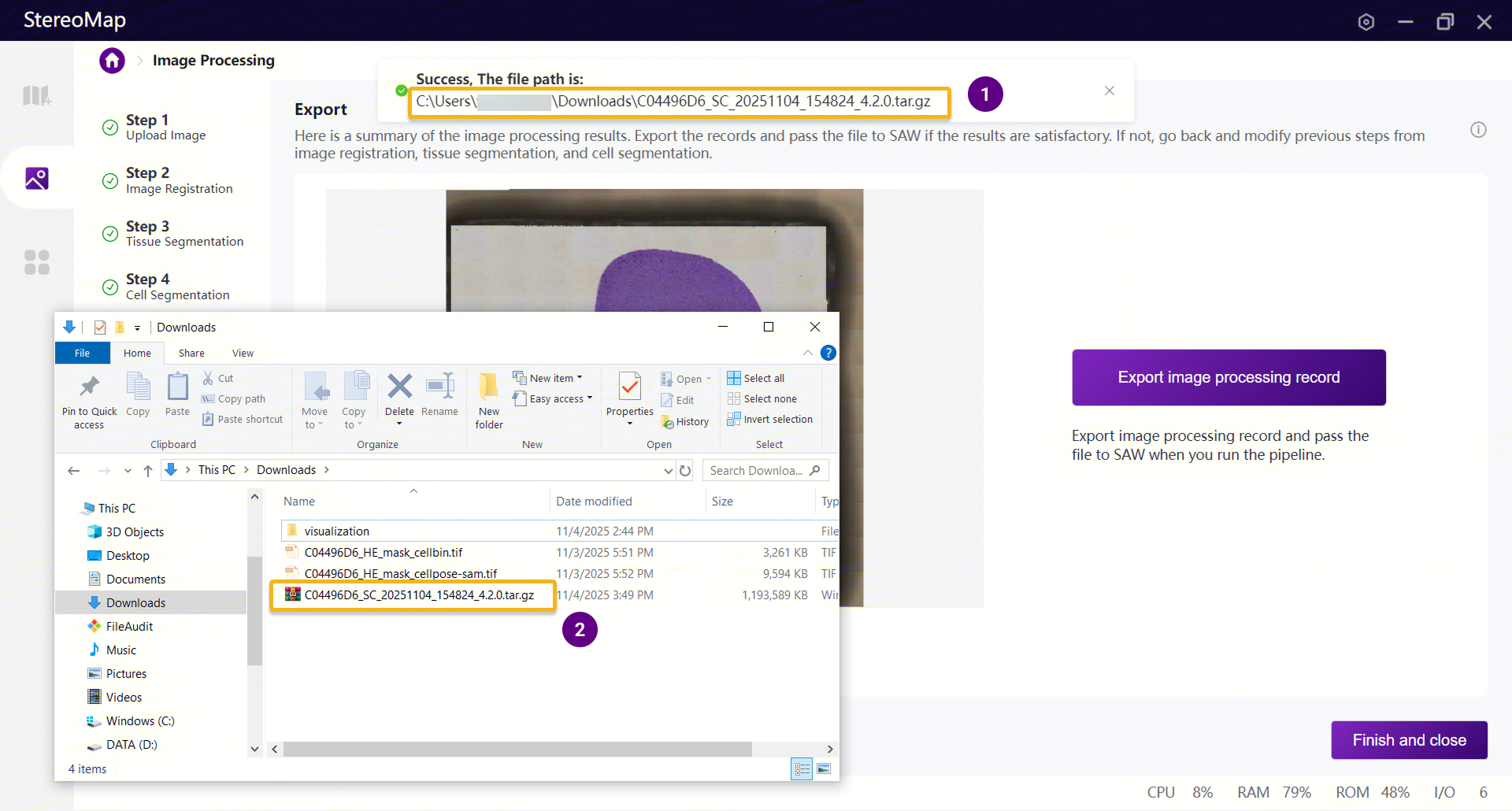
更新后的结果文件为替换了 mask 的图像
.tar.gz包。生成成功后,可在界面顶部的横幅通知中查看完整的输出路径。
重新计算 CellBin 矩阵
将 StereoMap 在本地导出的图像
.tar.gz包上传至部署了 SAW 的服务器,然后将其输入至 SAW 的realign流程。该流程将基于第三方算法生成的细胞分割结果重新提取 CellBin 矩阵。# 输入更新后的图像 .tar.gz 运行 saw realign流程,重新提取 CellBin 矩阵
saw realign \
--id=C04496D6_realign \
--sn=C04496D6 \
--count-data=C04496D6_Mouse_Brain \
--realigned-image-tar=C04496D6_SC_20251104_154824_4.2.0.tar.gz \
--threads-num=24需要注意的是,
--count-data参数应传入第 1 步中上传.stereo文件时所使用的 SAWcount分析结果目录。运行完成后,
outs目录中的.cellbin*.h5ad和.cellbin.gef文件即为基于第三方分割结果重新生成的细胞矩阵。同时,.html网页报告中的细胞统计与聚类结果,也根据这些更新后的矩阵重新计算。
outs
├── analysis
│ ├── ...
│ ├── C04496D6.cellbin_1.0.adjusted.h5ad
│ ├── C04496D6.cellbin_1.0.adjusted.marker_features.csv
│ ├── C04496D6.cellbin_1.0.h5ad
│ └── C04496D6.cellbin_1.0.marker_features.csv
├── bam
│ └── ...
├── C04496D6.report.html
├── feature_expression
│ ├── C04496D6.adjusted.cellbin.gef
│ ├── C04496D6.cellbin.gef
│ └── ...
├── image
│ ├── C04496D6_HE_mask_edm_dis_10.tif
│ ├── C04496D6_HE_mask.tif
│ └── ...
├── visualization.tar.gz
└── visualization.tar.gz.md5
5 directories, 23 files